

Citation: Guo Ye, Fu Lili, Fan Xiaowen, Shi Xuanling. Synthesis and Anti-HIV-1 Activity of Stapled HIV-1 Fusion Inhibitors[J]. Chinese Journal of Organic Chemistry, 2018, 38(5): 1267-1270. doi: 10.6023/cjoc201710033

构象锁定HIV-1融合抑制剂的合成及抗HIV-1活性研究
English
Synthesis and Anti-HIV-1 Activity of Stapled HIV-1 Fusion Inhibitors
-
Key words:
- sifuvirtide
- / HIV-1 fusion inhibitor
- / hydrocarbon stapling
- / anti-HIV-1 activity
-
西夫韦肽(Sifuvirtide, SFT)[1]是一种有效的HIV-1 (human immunodeficiency virus-1)融合抑制剂(fusion inhibitors). SFT含有36个氨基酸, 序列衍生于HIV-1 E亚型包膜糖蛋白gp41C端重复序列(C-terminal heptad repeat, CHR), 经计算机三维结构模拟分析后, 多肽序列中对于活性和稳定性无关的i和i+4位置氨基酸被替换成谷氨酸和精氨酸, 进而形成盐桥稳定结构, 并在C端引入谷氨酸N端引入丝氨酸增加SFT稳定性[2]. SFT较目前唯一由FDA (US Food and Drug Administration)批准上市的HIV-1多肽融合抑制剂T20 (Enfuvirtide)拥有以下优点[3~5]:抗HIV-1活性提高了约20倍, 克服T20单次注射剂量大问题, 降低用药费用; 在人体内的半衰期提高了约3.4倍, 克服了T20频繁注射问题, 提高了患者生活质量; 作用靶点与T20不同, 克服了T20耐药性的问题.目前, SFT已完成IIb临床试验, 并被证明抗HIV-1活性显著[6].因此, SFT被认为是继T20之后最有潜力成功上市的HIV-1融合抑制剂[7].在这一背景下, 发展具有更高抗HIV-1活性的SFT类似物成为当前HIV融合抑制剂研究的重要问题之一.本工作通过在SFT序列中引入构象锁定合成了一系列具有稳定α-螺旋结构的SFT订书肽, 并对其二级结构和抗HIV-1假病毒活性进行测试, 活性测试结果表明SFT订书肽对HIV-1标准株和中国流行株假病毒的抑制活性均高于SFT.
1. 结果与讨论
1.1 设计与合成
SFT二级结构被发现在溶液中是无规则卷曲结构, 而当体系中存在N36多肽(SFT作用靶点NHR区域截取序列)时, SFT可以与N36形成稳定的α-螺旋结构[2].据此实验结果, 我们推测SFT与靶点作用时需要由无规则卷曲结构变为α-螺旋结构.因此, 我们设计提前使SFT类似物形成稳定的α-螺旋结构, 降低其与靶点结合时构象变化所需能量来提高其抑制HIV-1的活性.
构象锁定是由Verdine组[8]发展用于合成具有α-螺旋结构多肽的主要方法之一.这种方法通过将多肽序列中i, i+4位置残基替换为侧链末端含有双键的非天然氨基酸S5, 再经烯烃复分解反应将两个S5侧链连接形成类似订书钉的结构促使多肽α-螺旋构象锁定.构象锁定较其它锁定策略具有显著提高多肽螺旋程度[9]、使用便捷(固相多肽合成所需的Fmoc-S5-OH已经商品化)[10]和应用范围广[11~14]的优点.这里, 我们选取构象锁定来合成具有α-螺旋结构的SFT类似物.我们设计在SFT序列中按照图 1所示分别进行1次锁定和2次锁定得到SFT-1和SFT-2. SFT-1中锁定引入的位置位于SFT序列中部暴露在溶剂面的用于形成盐桥结构的18位Arg和22位Glu. SFT-2中锁定引入的位置位于多肽的溶剂暴露面用于形成盐桥的两个位置18位Arg和22位Glu, 25位Glu和29位Arg.
图 1
目标多肽SFT-1使用Rink amide AM树脂通过标准Fmoc (9-fluorenyl-methyloxycarbonyl)固相多肽合成方法[15]进行合成(Scheme 1).按照设计引入锁定的位置分别将18位Arg和22位Glu替换为Fmoc-S5-OH在树脂上进行氨基酸缩合得到中间体1.然后使用Grubbs' 1代催化剂对中间体1进行烯烃复分解环关反应得到中间体2.对中间体2的N端进行乙酰化修饰后, 使用三氟乙酸(trifluoroacetic acid, TFA)切割试剂处理即可得到SFT-1.目标多肽SFT-2的合成采用与SFT-1类似的方法, 在第一个引入锁定的位置将两氨基酸全部替换为Fmoc-S5-OH后, 使用Grubbs' 1代催化剂处理进行第1次关环反应, 然后再进行剩余氨基酸的缩合.所有氨基酸在树脂上缩合完毕后再进行第2次关环反应、乙酰化修饰和切割得到SFT-2.经质谱鉴定及高效液相色谱(HPLC)纯化后得到纯度大于95%的SFT-订书肽SFT-1和SFT-2.
图式 1
1.2 二级结构
SFT和SFT订书肽均采用圆二光谱表征二级结构.如图 2所示, 圆二光谱中SFT订书肽在195 nm处有正吸收峰, 208和222 nm处有负吸收峰, 与文献[16]报道典型α-螺旋结构的特征吸收峰位置一致, 表明SFT订书肽均形成了α-螺旋结构.但SFT在以上三处特征吸收峰位置处无吸收, 在204 nm处有吸收峰, 表明SFT是以无规则卷曲构象存在, 这与He课题组[2]报道SFT是无规则卷曲结构一致.这一结果说明构象锁定可以使SFT形成稳定的α-螺旋结构.根据螺旋度计算公式[17]计算得到SFT-1和SFT-2的螺旋程度分别为43.3%和35.9%.SFT-1较SFT-2螺旋程度高说明只在多肽序列中18Arg和22Glu处引入C—H键锁定更有利于SFT形成α-螺旋结构.
图 2
1.3 抗HIV-1假病毒活性
通过测定HIV-1假病毒中携带的报告基因荧光素酶催化底物后产生化学反应的发光强度, 得到SFT和SFT订书肽抑制HIV-1假病毒标准株(JRFL和HXB2)和中国流行株(CNE6, CNE11, CNE15, CNE30和CNE5)的中和活性(表 1).由表 1可见, SFT对5个不同亚型HIV-1假病毒呈现纳摩尔级别的抑制活性, 这与文献报道SFT是广谱融合抑制剂一致. SFT订书肽也对7个HIV-1假病毒均表现出纳摩尔级别的抑制活性, 且活性整体高于SFT, 其中SFT-1对7个病毒株的抑制活性较SFT提高1.2~8.3倍, SFT-2的活性较SFT提高1.0~7.8倍.这可能是由于SFT订书肽预先形成稳定的α-螺旋结构减少了与靶点结合时的熵消耗, 从而提高其抗HIV-1假病毒中和活性.对SFT-1和SFT-2抗HIV-1假病毒活性进行统计学分析, 发现SFT-1对CNE6、CNE11、CNE15和CNE30假病毒株的抑制活性显著高于SFT(P<0.05), 活性差异具有统计学意义, SFT-2对HXB2、JRFL、CNE15、CNE30和CNE5假病毒抑制活性显著高于SFT (P<0.05), 活性差异具有统计学意义.对比新合成融合抑制剂SFT锁定多肽对假病毒的抑制活性发现SFT-1对CNE6, CNE11和CNE15病毒株的抑制活性最强, 而SFT-2对JRFL和HXB2 CNE30和CNE5病毒株的抑制活性最强, 具体的构象锁定位置不同对于SFT结构和活性的影响有待进一步研究.
表 1
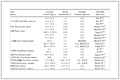 表 1 SFT和SFT-订书肽抗HIV-1假病毒活性aTable 1. Inhibitory activity of SFT and SFT-stapled peptide against HIV-1 pseudovirus
表 1 SFT和SFT-订书肽抗HIV-1假病毒活性aTable 1. Inhibitory activity of SFT and SFT-stapled peptide against HIV-1 pseudovirusPseudovirus Subtype IC50/(nmol•L-1) P1 t1 IC50/(nmol•L-1) P2 t2 SFT SFT-1 SFT-2 HXB2 B 0.47±0.13 0.27±0.04 0.064 2.547 0.14±0.04 * 0.014 4.202 JRFL B 8.18±1.29 5.88±1.48 0.112 2.029 1.92±1.01 * 0.003 6.618 CNE6 B' 4.04±0.55 1.98±0.56 * 0.010 4.546 3.74±1.12 0.698 0.416 CNE11 B' 7.38±1.31 4.57±0.72 * 0.031 3.256 7.45±2.24 0.956 0.047 CNE15 B'C 40.04±1.77 4.84±1.10 * 0.000 29.254 5.12±0.16 0.000 34.033 CNE30 CRF08_BC 51.05±5.15 29.67±4.27 0.005 5.535 18.89±4.82 * 0.001 7.897 CNE5 CRF01_AE 7.36±0.08 6.25±1.71 0.324 1.123 4.48±1.77 * 0.048 2.815 a 每个多肽的抑制活性均被测量3次; *表示活性最高多肽; P1和t1, P2和t2分别对应于SFT和SFT-1, SFT和SFT-2的统计学分析. 2. 结论
采用构象锁定方法, 以Fmoc保护氨基酸为原料, 经过多肽固相缩合反应合成出了SFT及新的SFT类似物SFT订书肽.目标化合物的圆二光谱证明所合成的SFT订书肽均具有α-螺旋结构, 其中SFT-1的螺旋程度最高.抗HIV-1假病毒活性研究表明SFT订书肽对7个假病毒的抑制活性整体高于SFT, 其中SFT-1抗CNE6, CNE5和CN15的活性较SFT显著提升了1.6~8.3倍, SFT-2抗CNE30, CNE5-CRF01, JRFL和HXB2的活性较SFT显著提升1.6~4.3倍.综合分析圆二色谱和抗HIV-1假病毒活性数据表明提高SFT的螺旋性可以提高其对6种不同亚型HIV-1假病毒的抑制活性.
3. 实验部分
3.1 仪器与试剂
高效液相色谱为岛津高效液相色谱, 质谱仪为Agilent 1200型. Fmoc保护的氨基酸购自上海吉尔生化生物科技公司, Fmoc-S5-OH购自北京欧凯纳斯试剂公司, Rink amide树脂购自天津南开合成, 其余试剂均为市售分析纯. HIV全长膜蛋白质粒pcDNA3.1+购自Invitrogen.
3.2 实验方法
3.2.1 SFT的合成
使用200 mg Rink amide树脂(取代度为0.3 mmol·g-1)通过Fmoc固相合成技术合成SFT, 氨基酸的投量为4 equiv., 缩合剂HCTU [O-(6-Chlorobenzotriazol-1-yl)-N, N, N', N'-tetramethyluronium hexafluorophosphate]的投量为3.8 equiv., DIEA (N, N-diisopropylethylamine)的投量为8 equiv.[18~20].待多肽在树脂上组装完毕后, 脱去最后一个氨基酸的Fmoc保护基使用3 mL含10%醋酸酐(0.3 mL)和10% DIEA (0.3 mL)的DMF (N, N-dimethylfor-mamide)溶液对其进行乙酰化修饰.反应10 min后, 洗涤树脂并加入10 mL含2.5%水(0.25 mL), 2.5% TIPS (0.25 mL)的TFA切割试剂反应3 h. N2处理切割试剂后, 加入冰乙醚沉淀得到白色粉末状粗肽, 使用HPLC和ESI-MS对其进行分析鉴定和纯化, 得到73.1 mg白色絮状固体, 分离产率为25.8%. ESI-MS m/z: 4726.9 ([M+H]+), 1576.3 ([M+3H]3+), 1182.5 ([M+4H]4+), 946.3 ([M+5H]5+), 788.7 ([M+6H]6+).
3.2.2 SFT-1的合成
使用与合成SFT相同投量的树脂, 氨基酸和缩合剂通过Fmoc固相合成技术制备SFT-1.缩合Fmoc-S5-OH时, 氨基酸的投量为2 equiv., HATU [O-(7-azabenzo-triazol-1-yl)-N, N, N', N'-tetramethyluronium hexafluorophosphate]的投量为1.9 equiv., HOAt (1-hydroxy-7-aza-benzotriazole)的投量为2 equiv., DIEA的投量为4 equiv., 反应时间为2 h.待所有氨基酸组装完毕后, 加入21 mg Grubbs' 1代催化剂的二氯甲烷(dichloromethane, DCM)溶液避光反应2 h.烯烃复分解反应结束后再进行乙酰化修饰, 切割.经HPLC和ESI-MS对其进行分析鉴定和纯化后得到59.5 mg白色絮状固体, 分离产率为21.4%. ESI-MS m/z: 4635.1 ([M+H]+), 1545.7 ([M+3H]3+), 1159.6 ([M+4H]4+), 927.9 ([M+5H]5+).
3.2.3 SFT-2的合成
使用与合成SFT-1相同投量的树脂, 氨基酸, Fmoc-S5-OH和缩合剂通过Fmoc固相合成技术制备SFT-2.待前两个Fmoc-S5-OH缩合完毕后, 加入21 mg Grubbs’1代催化剂的DCM溶液进行第一次烯烃复分解反应.反应后洗涤树脂继续进行剩余氨基酸的缩合.所有氨基酸缩合完毕后, 再次加入Grubbs' 1一代催化剂进行第二次烯烃复分解反应.反应结束后进行乙酰化修饰, 切割.经HPLC和ESI-MS对其进行分析鉴定和纯化后得到51.9 mg白色絮状固体, 分离产率为18.6%. ESI-MS m/z: 4657.6 ([M+H]+), 1553.2 ([M+3H]3+), 1165.2([M+4H]4+), 932.3 ([M+5H]5+).
3.2.4 二级结构测定
将SFT, SFT-1和SFT-2分别溶于1X磷酸盐缓冲溶液(pH 7.4)中配制为50 μmol/L的待测样品.样品池为1 mm的石英比色皿. Jasco-715圆二光谱仪的测量参数为波长185~260 nm, 步长0.5 nm, 带宽1 nm, 累计收集3次数据.在25 ℃下, 使用圆二色谱仪分别采集SFT, SFT-1和SFT-2的椭圆度数据, 并根据螺旋度计算公式计算各多肽的螺旋度.
3.2.5 抗HIV-1假病毒活性测试
将SFT, SFT-1和SFT-2溶于二甲基亚砜(DMSO)中分别制备为1 mg/L储存液.使用CNE6, CNE11, CNE15, CNE30, CNE5, JRFL, HXB2 HIV-1假病毒(含有荧光素酶报告基因)检测系统分别对3条多肽检测, 通过测定HIV-1假病毒中携带的报告基因荧光素酶催化底物后, 产生化学反应的发光强度, 得到多肽抑制HIV-1假病毒感染易感细胞GHOST(3)X4/R5的中和活性.将不同浓度的SFT, SFT-1和SFT-2置于96孔板中, 每孔加入200 TCID50 (50% tissue culture infectious dose)的HIV-1假病毒, 同时设立空白对照组和阴性对照组, 再将96孔板置于37 ℃恒温培养箱中孵化1 h.抑制剂作用后, 每孔加入100 μL已处理好的GHOST(3)X4/R5细胞(1.5×105个•mL-1), 继续孵化60 h.弃去96孔板中上清培养基, 加入100 μL新鲜磷酸盐缓冲溶液和50 μL荧光素酶检测试剂避光反应2 min; 裂解96孔板中的细胞, 使用化学发光仪测定发光强度, 并计算抑制率.
辅助材料(Supporting Information) SFT, SFT-1和SFT-2的MS和HPLC谱图.这些材料可以免费从本刊网站(http://sioc-journal.cn/)上下载.
-
-
[1]
Dai, S. J.; Dou, G. F.; Qiang, X. H.; Song, H. F.; Tang, Z. M.; Liu, D. S.; Liu, X. W.; Yang, L. M.; Zheng, Y. T.; Liang, Q. Acta Pharmacol. Sin. 2005, 26, 1274. doi: 10.1111/aphs.2005.26.issue-10
-
[2]
He, Y.; Xiao, Y.; Song, H.; Liang, Q.; Ju, D.; Chen, X.; Lu, H.; Jing, W.; Jiang, S.; Zhang, L. J. Biol. Chem. 2008, 283, 11126. doi: 10.1074/jbc.M800200200
-
[3]
Tan, J. J.; Ma, X. T.; Liu, C.; Zhang, X. Y.; Wang, C. X. Curr. Pharm. Des. 2013, 19, 1810. doi: 10.2174/1381612811319100005
-
[4]
Tennyson, R. L.; Walker, S. N.; Ikeda, T.; Harris, R. S.; Kennan, A. J.; McNaughton, B. R. ChemBioChem 2016, 17, 1945. doi: 10.1002/cbic.v17.20
-
[5]
Zhang, D.; Li, W.; Jiang, S. Expert. Opin. Ther. Pat. 2015, 25, 159. doi: 10.1517/13543776.2014.987752
-
[6]
Yu, F.; Lu, L.; Du, L. Y.; Zhu, X. J.; Debnath, A. K.; Jiang, S. B. Viruses 2013, 5, 127. doi: 10.3390/v5010127
-
[7]
Yao, X.; Chong, H.; Zhang, C.; Waltersperger, S.; Wang, M.; Cui, S.; He, Y. J. Biol. Chem. 2012, 287, 6788. doi: 10.1074/jbc.M111.317883
-
[8]
Schafmeister, C. E.; Po, J.; Verdine, G. L. J. Am. Chem. Soc. 2000, 122, 5891. doi: 10.1021/ja000563a
-
[9]
Wachter, F.; Morgan, A. M.; Godes, M.; Mourtada, R.; Bird, G. H.; Walensky, L. D. Oncogene 2017, 36, 2184. doi: 10.1038/onc.2016.361
-
[10]
Bird, G. H.; Mazzola, E.; Opoku-Nsiah, K.; Lammert, M. A.; Godes, M.; Neuberg, D. S.; Walensky, L. D. Nat. Chem. Biol. 2016, 12, 845. doi: 10.1038/nchembio.2153
-
[11]
高帅, 郭叶, 李海燕, 方葛敏, 化学进展, 2014, 26, 100. doi: 10.1007/s11069-014-1109-4Gao, S.; Guo, Y.; Li, H. Y.; Fang, G. M. Prog. Chem. 2014, 26, 100(in Chinese). doi: 10.1007/s11069-014-1109-4
-
[12]
Hu, X.; He, Y.; Wu, L.; Hao, Y.; Wang, Z.; Zheng, W. Bioorg. Med. Chem. Lett. 2017, 27, 5446. doi: 10.1016/j.bmcl.2017.10.076
-
[13]
Cui, H. K.; Qing, J.; Guo, Y.; Wang, Y. J.; Cui, L. J.; He, T. H.; Zhang, L. Q.; Liu, L. Bioorg. Med. Chem. 2013, 21, 3547. doi: 10.1016/j.bmc.2013.02.011
-
[14]
Cui, H. K.; Zhao, B.; Li, Y.; Guo, Y.; Hu, H.; Liu, L.; Chen, Y. G. Cell Res. 2013, 23, 581. doi: 10.1038/cr.2013.30
-
[15]
Lau, Y. H.; de Andrade, P.; Wu, Y.; Spring, D. R. Chem. Soc. Rev. 2015, 44, 91. doi: 10.1039/C4CS00246F
-
[16]
Keeling, K. L.; Cho, O.; Scanlon, D. B.; Booker, G. W.; Abell, A. D.; Wegener, K. L. Org. Biomol. Chem. 2016, 14, 9731 doi: 10.1039/C6OB01745B
-
[17]
Wang, D. Y.; Chen, K.; Kulp Ⅲ, J. L.; Arora, P. S. J. Am. Chem. Soc. 2006, 128, 9248. doi: 10.1021/ja062710w
-
[18]
Fang, G. M.; Wang, J.-X.; Liu, L. Angew. Chem., Int. Ed. 2012, 51, 10347. doi: 10.1002/anie.201203843
-
[19]
Fang, G. M.; Li, Y. M.; Shen, F.; Huang, Y. C.; Li, J. B.; Lin, Y.; Cui, H. K.; Liu, L. Angew. Chem., Int. Ed. 2011, 50, 7645. doi: 10.1002/anie.201100996
-
[20]
Zheng, J. S.; Tang, S.; Qi, Y. K.; Wang, Z. P.; Liu, L. Nat. Protoc. 2013, 8, 2483. doi: 10.1038/nprot.2013.152
-
[1]
-
表 1 SFT和SFT-订书肽抗HIV-1假病毒活性a
Table 1. Inhibitory activity of SFT and SFT-stapled peptide against HIV-1 pseudovirus
Pseudovirus Subtype IC50/(nmol•L-1) P1 t1 IC50/(nmol•L-1) P2 t2 SFT SFT-1 SFT-2 HXB2 B 0.47±0.13 0.27±0.04 0.064 2.547 0.14±0.04 * 0.014 4.202 JRFL B 8.18±1.29 5.88±1.48 0.112 2.029 1.92±1.01 * 0.003 6.618 CNE6 B' 4.04±0.55 1.98±0.56 * 0.010 4.546 3.74±1.12 0.698 0.416 CNE11 B' 7.38±1.31 4.57±0.72 * 0.031 3.256 7.45±2.24 0.956 0.047 CNE15 B'C 40.04±1.77 4.84±1.10 * 0.000 29.254 5.12±0.16 0.000 34.033 CNE30 CRF08_BC 51.05±5.15 29.67±4.27 0.005 5.535 18.89±4.82 * 0.001 7.897 CNE5 CRF01_AE 7.36±0.08 6.25±1.71 0.324 1.123 4.48±1.77 * 0.048 2.815 a 每个多肽的抑制活性均被测量3次; *表示活性最高多肽; P1和t1, P2和t2分别对应于SFT和SFT-1, SFT和SFT-2的统计学分析. -

 扫一扫看文章
扫一扫看文章
计量
- PDF下载量: 3
- 文章访问数: 1493
- HTML全文浏览量: 214

 下载:
下载:


 下载:
下载:
 下载:
下载:

